根据国际数据公司(IDC)的预测,到2025年,全球数据量将达到175泽字节(ZB),相当于每个人每天产生约1.7 MB的数据。这种全球性的数据激增带来了一个巨大的挑战:如何高效、可持续地存储如此庞大的信息?
目前,传统的硬盘、固态硬盘和云存储是数据存储的主要方式。然而,它们的局限性也日益凸显。例如,硬盘和固态硬盘的存储密度增长速度赶不上数据增长的速度。这些传统存储介质的使用寿命一般也只有数年,需要频繁更换,增加了成本和资源消耗。此外,全球数据中心的能耗已经占到了全球总能耗的1%以上,这不仅耗费大量能源,还对环境产生了不利影响。
那么,有没有一种方式,既能高密度存储庞大的数据,又能长时间保持数据的完整性,同时还节能环保呢?
科学家们将目光投向了生命的载体——DNA。
DNA,作为遗传信息的载体,具有天然的优势:
• 超高储存密度:一克DNA理论上可以存储约215 PB(拍字节)的数据,相当于可以容纳 1千万小时的高清视频内容。
• 超长保存时间:在适宜的条件下(比如避免接触湿气和紫外线,因为它们会破坏分子结构),DNA 的化学稳定性允许其保存数十万年。
• 环境友好:DNA是一种不需要持续供电的存储介质,能耗极低,有助于降低数据存储对环境的影响。
那么DNA如何储存信息呢?
我们可以把DNA想象成一本由四个字母组成的书,这四个字母分别是A(腺嘌呤)、T(胸腺嘧啶)、C(胞嘧啶)和G(鸟嘌呤),也就是四种碱基。这四种碱基各自与脱氧核糖和磷酸结合可形成相应的核苷酸,然后再通过不同的排列组合,形成了DNA的序列,就像文字的组合构成了书中的内容。在生物体中,这些序列编码了遗传信息,指导着生命的生长、发育和功能。
在数据存储中,科学家们借鉴了这一原理,将数字信息转换为DNA的碱基序列。例如,可以将二进制的“0”和“1”对应到特定的碱基上,或者通过特定的编码规则,将数据映射为一段DNA序列。但问题是传统方法需要从头合成新的DNA链,这一过程既昂贵又缓慢。此外,长链DNA合成也容易出错,影响数据的准确性和可靠性。
那我们是否有办法突破这些瓶颈呢?
2024年10月23日,在一篇发表于《自然》杂志上的论文中,一个由中国科学家领导的团队受到表观遗传学的启发,开发了一种用DNA储存数据的新技术——“表观比特”储存技术。
什么是表观遗传学呢?我们继续把DNA想象成一本书,里面的文字代表我们的基因信息。表观遗传学就好比在这本书的特定文字上做标记(如加粗、下划线),不改变文字本身,但可以影响对内容的理解和解读。
在生物学中,表观遗传修饰通过在DNA的特定碱基上添加或移除化学基团,比如甲基(CH₃),来调节基因的表达。这种调节可以影响细胞功能,甚至决定基因是否被“打开”或“关闭”。
研究人员利用了DNA链上特定碱基的甲基化和去甲基化来表示二进制信息:
•甲基化的碱基:表示二进制的“1”。
•未甲基化的碱基:表示二进制的“0”。
这种“表观比特”类似于传统的比特。这种新技术不依赖于从头合成DNA,而是利用现有的DNA分子进行数据存储,就像在纸上印刷文字一样,无需重新制造纸张。
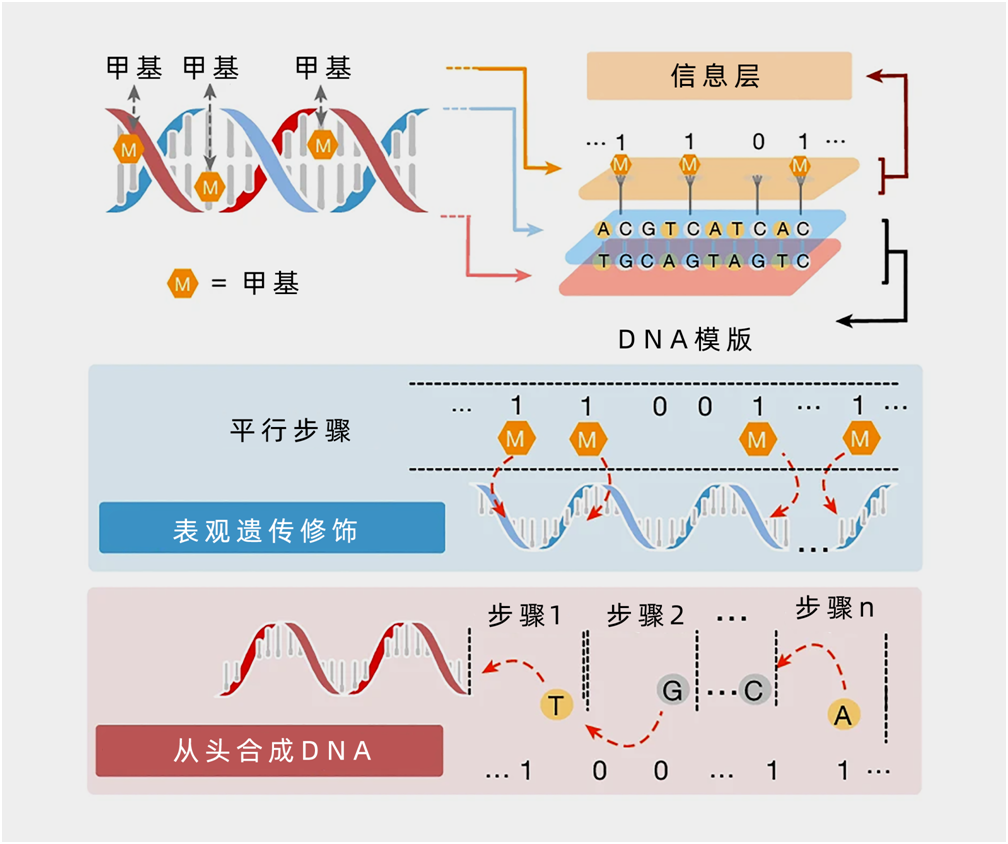
表观遗传信息储存的机制。 图:ChengZhang et al.
在论文中,研究人员提出了一种基于并行写入策略的DNA储存策略。他们设计并预制了一个通用的单链DNA载体,可以看作是数据存储的“纸张”。他们还设计了一系列互补的短单链DNA,称为“文字库”,这些短链DNA能够与载体的特定位置配对结合,就像印刷活字中的字模。通过将“文字库”加载到DNA载体的相同位置上,可以排列组合出所需的“表观比特”信息,类似于将活字排版在印刷版上。
接下来,利用酶的作用,就可以对DNA载体上的特定碱基进行甲基化修饰。这种选择性甲基化是并行进行的,意味着可以同时在多个位置上进行修饰,大幅提高效率。通过上述步骤,数据被稳定地“打印”在DNA载体上,完成了一次精密而高效的“分子印刷术”。
在实验中,研究团队仅使用了700种DNA活字和5个DNA模板,通过不同的组合,就可以编程出大量的数据。在自动化的实验平台上,他们实现了约27.5万个比特的数据写入,每次反应可以写入350比特的数据。
新研究表明,DNA存储的潜力正在逐渐显现。凭借其高密度、长寿命和低能耗的特点,DNA或许能成为未来解决数据存储危机的关键。在这条探索的道路上,“表观比特”技术迈出了重要一步,让人类看到了自然智慧与科技创新结合的无限可能。
或许有一天,我们真的可以将全人类的知识和记忆,凝聚在微小的DNA分子中。
本文为科普中国·创作培育计划扶持作品
作者名称:沈雯
审核:梁前进 北京师范大学生命科学学院 教授
出品:中国科协科普部
监制:中国科学技术出版社有限公司、北京中科星河文化传媒有限公司

来源: 星空计划
内容资源由项目单位提供


 科普中国公众号
科普中国公众号
 科普中国微博
科普中国微博

 帮助
帮助
 科普中国创作培育计划
科普中国创作培育计划 
